Prozesse vernetzen: Strukturanalyse im NRW-Verbund
Deutsche Forschungsgemeinschaft (DFG) fördert Gerätezentrum
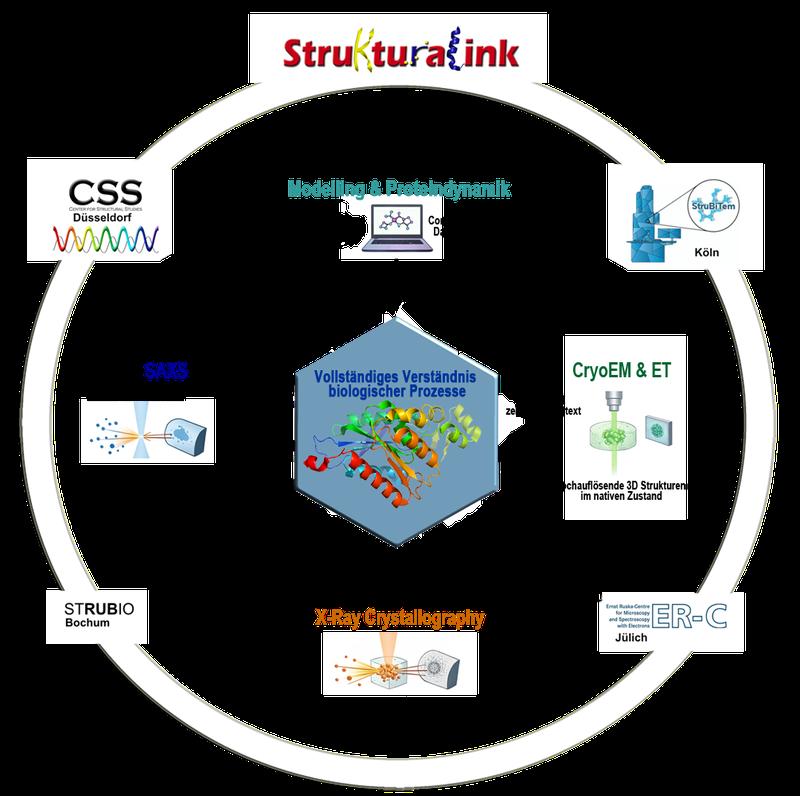
Um biologische Prozesse zu verstehen, muss sehr oft erst die dreidimensionale Struktur der beteiligten Moleküle entschlüsselt werden – ein komplexer Vorgang, welcher umfangreicher Geräte und großer Expertise bedarf. Im Verbund „StrukturaLink Rhein-Ruhr“ wird unter der Leitung der Heinrich-Heine-Universität Düsseldorf (HHU) moderne Strukturbiologie miteinander vernetzt. Beteiligt sind weiterhin die Universitäten in Bochum und Köln sowie das Forschungszentrum Jülich. Das Projekt wird für fünf Jahre mit insgesamt 1,1 Millionen Euro gefördert.
Viele zentrale Prozesse des Lebens spielen sich auf molekularer Ebene ab. Proteine falten sich, binden aneinander, ändern ihre Struktur. Ihre Struktur bestimmt, wie Zellen funktionieren und sich anpassen; Krankheitserreger nutzen spezifische Molekülstrukturen, um in Zellen einzudringen; aber auch fehlerhafte Strukturen selbst können krank machen, wie zum Beispiel bei der die Sichelzellenanämie des Hämoglobins.
In der Vergangenheit haben Forschende des Verbundes entschlüsselt, wie Mehltaupilze ihre Angriffsmoleküle verändern, um die Abwehr von Getreide zu umgehen. Dabei entdeckten sie eine gemeinsame Struktur, welche das Verständnis der pflanzlichen Immunerkennung deutlich verbessert
Um alle diese Prozesse zu verstehen, braucht es eine Vielzahl verschiedener strukturbiologischer Methoden, denn keine einzelne Technik kann allein die Komplexität biologischer Prozesse erfassen. Hier setzt „StrukturaLink Rhein-Ruhr“ an: Das neu von der DFG geförderte sogenannte Gerätezentrum vernetzt modernste strukturbiologische Technologien und Expertise an vier Standorten in Nordrhein-Westfalen miteinander. Verfolgt wird ein integrativer Ansatz: Hochauflösende Kryo-Elektronenmikroskopie (Cryo-EM) und Kryo-Elektronentomographie (Cryo-ET), Röntgenkristallographie, Small-Angle-X-ray-Scattering (SAXS) sowie computergestützte Modellierung und Protein-Dynamik-Berechnungen werden gezielt kombiniert, um biologische Prozesse umfassend analysieren zu können.
Prof. Dr. Sander Smits, Leiter des Center for Structural Studies (CSS) der HHU, ist Sprecher des Verbundes: „Jede dieser Methoden liefert unterschiedliche, sich ergänzende Informationen, erst ihr Zusammenspiel ermöglicht ein vollständiges strukturelles und funktionelles Verständnis.“
In Düsseldorf liegt der Fokus unter anderem auf SAXS-Analysen und molekularer Modellierung, mit denen flexible und dynamische Proteinkomplexe in Lösung untersucht werden können. Köln bietet hochauflösende Cryo-EM mit speziellen Möglichkeiten zur Probenpräparation. Bochum verfügt über besondere Expertise in der Röntgenstrukturanalyse sowie über spezialisierte Probenvorbereitung für sauerstoffempfindliche Proteine. In Jülich schließlich steht mit dem Ernst Ruska-Centrum eine Infrastruktur für Cryo-EM und Cryo-ET zur Verfügung, die für die strukturelle Zellbiologie von zentraler Bedeutung ist.
Ein zentrales Element von StrukturaLink ist das „Super-User-Konzept“: Speziell ausgebildete Wissenschaftlerinnen und Wissenschaftler sind an allen Standorten Ansprechpartner und begleiten Projekte von der Planung bis zur Auswertung. So werden komplexe Methoden effizient genutzt und Engpässe in der praktischen Umsetzung vermieden. Neben der Forschung setzt der Verbund gezielt auf Ausbildung und Wissenstransfer. Ergänzend werden gemeinsame Nutzungs- und Datenkonzepte etabliert, um die Forschung nachhaltig zu unterstützen.
„Mit diesem gemeinsamen Projekt intensivieren wir unsere langjährige Zusammenarbeit. Indem wir Expertise und Infrastruktur vernetzen, können wir strukturelle Fragestellungen über einzelne Institutionen hinaus bearbeiten, auf einem wissenschaftlichen Niveau, das nur im Verbund erreichbar ist“, betont Smits.
Kooperationspartner
An „StrukturaLink Rhein-Ruhr“ sind die Heinrich-Heine-Universität Düsseldorf, die Universität zu Köln, die Ruhr-Universität Bochum sowie das Forschungszentrum Jülich beteiligt. Neben Sprecher Prof. Dr. Sander Smits sind die weiteren Standortsprecher: Prof. Dr. Elmar Behrmann (Köln), Prof. Dr. Eckhard Hofmann (Bochum) und Prof. Dr. Carsten Sachse (Forschungszentrum Jülich). Sie alle bringen unterschiedliche Expertisen in der Strukturanalyse in den Verbund ein.
Langfristig soll der Verbund über die vier Standorte hinauswirken und weiteren Forschungseinrichtungen in Nordrhein-Westfalen offenstehen. So soll eine leistungsfähige, regionale Infrastruktur aufgebaut werden, die exzellente strukturbiologische Forschung ermöglicht, Kooperationen stärkt und die internationale Sichtbarkeit des Forschungsstandorts Rhein-Ruhr nachhaltig erhöht.
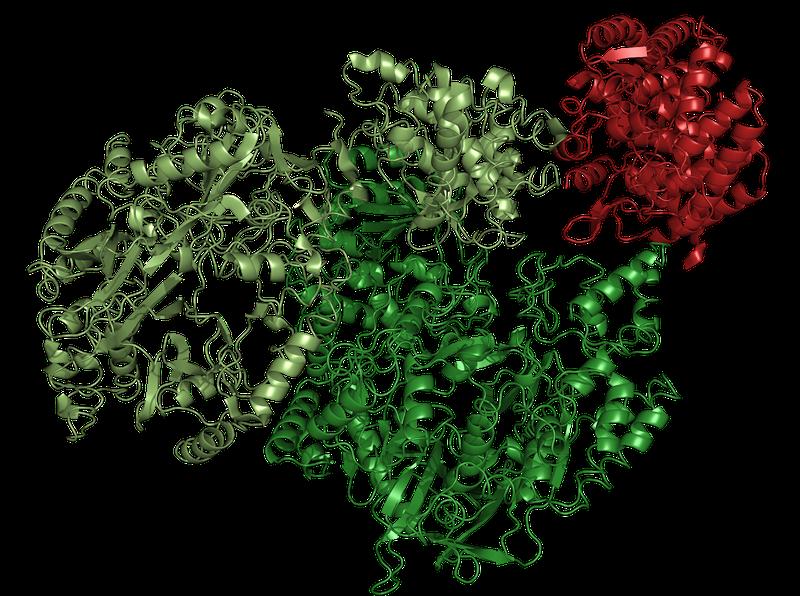
Ausführliche Bildunterschrift zu Bild 2:
Ergebnis einer Strukturaufklärung, bei der mehrere Methoden kombiniert wurden. Zu sehen ist der Enzymkomplex (MadB2C) des Bakteriums Clostridium maddingley, der zur Reifung des Peptid-Antibiotikums Maddinglicin dient. Mittels Röntgenkristallographie wurde die Struktur des rot dargestellten Teils (MadC) entschlüsselt, während die Struktur des grünen Teil (MadB) mithilfe hochauflösender Cryo-Elektronenmikroskopie bestimmt wurde. Anschließend wurden beide Datensätze computergestützt zu einem Gesamtmodell zusammengefügt. (Bild: HHU / CSS)
Ähnliche Pressemitteilungen im idw